Simulador 3D de Migración Celular Embrionaria
Simulación 3D de migración colectiva de Células de Formación Profunda sobre la superficie de un embrión esférico de pez cebra durante la epibolía. Usa sistema de coordenadas AER con streaming WebSocket y visualización Three.js.
Contexto de Negocio
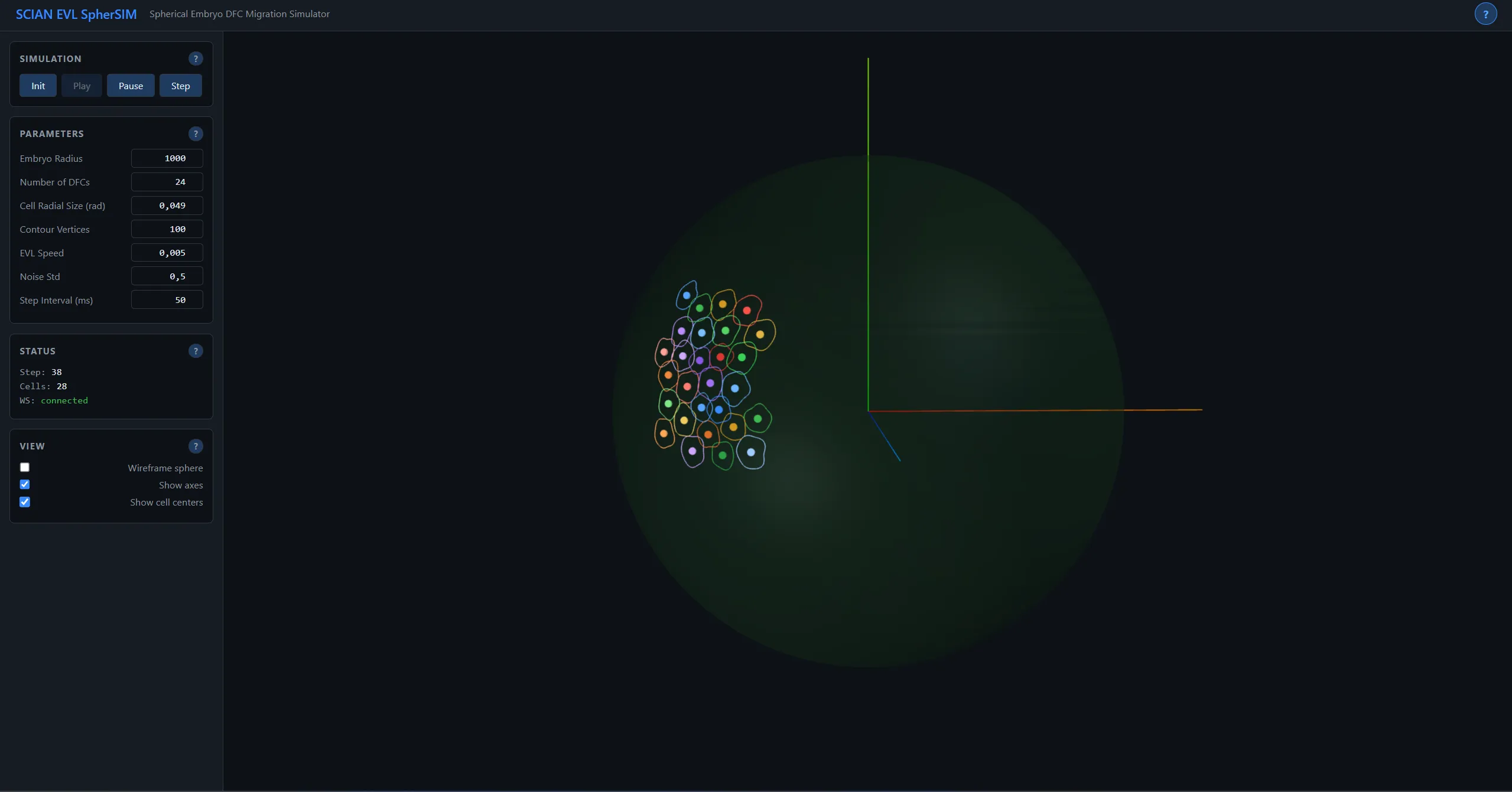
Durante la gastrulación del pez cebra, la Capa Envolvente se expande para envolver la célula de yema en un proceso llamado epibolía — uno de los movimientos morfogenéticos fundamentales en el desarrollo vertebrado. Las Células de Formación Profunda se desplazan con esta expansión, migrando colectivamente sobre la superficie curva del embrión. Simular este proceso en un plano 2D plano introduce distorsiones geométricas que comprometen la precisión biológica — la geometría esférica del embrión es esencial para entender la dinámica de migración.
Valor Estratégico
La simulación usa un sistema de coordenadas AER (Azimut-Elevación-Radio) naturalmente adecuado para geometría esférica, con wrapping periódico en azimut y clamping polar en elevación. La velocidad celular combina acoplamiento determinístico EVL con variabilidad biológica estocástica Gaussiana. Detección de colisiones por pares en espacio angular con resolución simétrica push-apart preserva el balance de momentum. Visualización Three.js con controles de órbita permite exploración 3D del embrión. Streaming WebSocket provee estado de simulación en tiempo real. Desarrollado en SCIAN-Lab, Universidad de Chile.
El Desafío
Simular migración celular colectiva en una superficie embrionaria curva requiere sistemas de coordenadas que manejen geometría esférica — singularidades polares, wrapping periódico — manteniendo detección de colisiones y resolución de fuerzas físicamente significativas.
Nuestro Enfoque
Sistema de coordenadas AER (Azimut-Elevación-Radio) con wrapping automático en los polos. El acoplamiento EVL provee velocidad base determinística; término estocástico Gaussiano agrega ruido biológico. Detección de colisiones por pares en espacio angular con resolución simétrica push-apart y proyección esférica. Streaming WebSocket para visualización 3D en tiempo real.
Indicadores Clave de Rendimiento
| KPI | Línea Base | Resultado | Impacto |
|---|---|---|---|
| Geometría | Simulaciones 2D planas | Superficie 3D esférica de embrión | Geometría biológicamente precisa |
| Visualización | Renderizado offline | Three.js WebGL en tiempo real | Exploración 3D interactiva |
Arquitectura
sphersim
The Process
During zebrafish gastrulation, the Enveloping Layer (EVL) expands to engulf the yolk cell in a process called epiboly. Deep Forming Cells (DFCs) ride this expansion, migrating collectively on the curved embryo surface. This simulation captures that process on the actual spherical geometry of the embryo — not a flat approximation.
Spherical Coordinates
The AER (Azimuth-Elevation-Radius) coordinate system handles the geometry naturally. Azimuth wraps periodically (-π to π) — moving past one side means appearing on the other. Elevation clamps at the poles (-π/2 to π/2). Radius stays constant — cells are confined to the embryo surface.
Each cell’s velocity combines a deterministic component from EVL coupling (base_velocity = [0, -(π/2)·evl_speed, 0] — the expanding EVL drags cells vegetally) with a Gaussian stochastic term adding biological variability. Collision detection operates in angular space with symmetric push-apart resolution: overlapping cells are displaced equally in opposite directions, then projected back onto the sphere.
Three.js visualization with orbit controls lets researchers rotate, zoom, and inspect the 3D embryo from any angle. WebSocket streaming provides real-time simulation state. Play/Pause/Step controls enable frame-by-frame inspection of migration dynamics.
Stack Tecnológico
Capturas de la Aplicación
Diagramas Técnicos
evl spring coupling
sphersim coordinates
sphersim epiboly
sphersim model